表观基因组关联研究数据库EWAS Data Hub,甲基化数据的高效查询so easy!
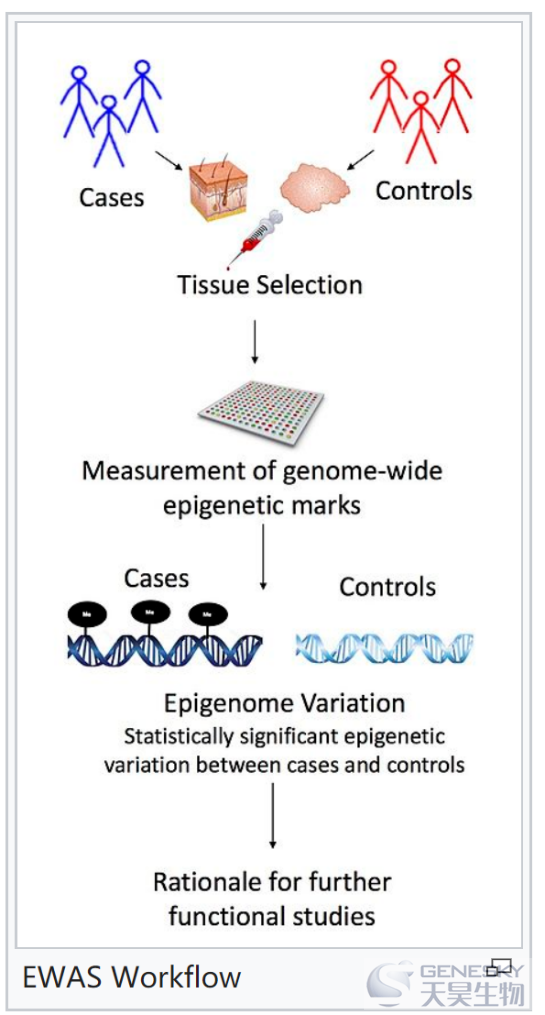
表观基因组关联分析(Epigenome-wide Association Study,EWAS),即基于全基因组范围寻找组间的表观遗传学标记的差别或特征,目前是研究复杂疾病遗传学基础的一种有效方法。由于DNA样本的易获得性和DNA甲基化检测技术的不断成熟,大量的科研成果已经累积了大量的DNA甲基化芯片数据(主要是Infinium HumanMethylation450 (450K) 和 MethylationEPIC (850K) 芯片平台)。有效的数据整合和深入挖掘,将为复杂疾病或性状的表观遗传学深入研究提供更多重要的参考信息。但是,由于不同试验的研究平台,研究批次,包括样本的年龄性别等信息千差万别,直接使用这些数据肯定会导致大量的假阳性。为了解决这些问题,实现更好的甲基化数据整合分析,中国科学院北京基因组研究所国家基因组科学数据中心,开发了人类表观组关联分析数据库EWAS Data Hub。该研究成果于2019年10月在国际学术期刊《核酸研究》(Nucleic Acids Research)在线发表,标题为“EWAS Data Hub: a resource of DNA methylation array data and metadata”。
图:EWAS试验流程
图:EWAS文章发表情况
● 数据库链接:
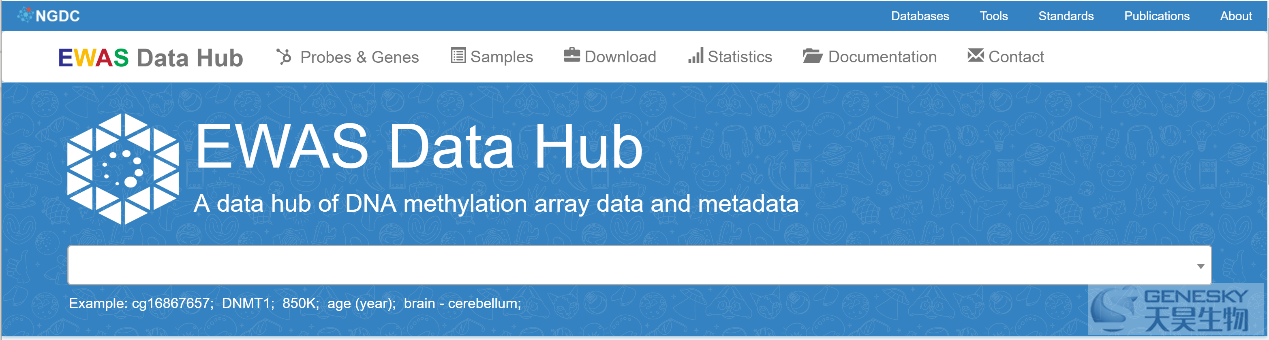
https://bigd.big.ac.cn/ewas/datahub/index
● 数据库内容:
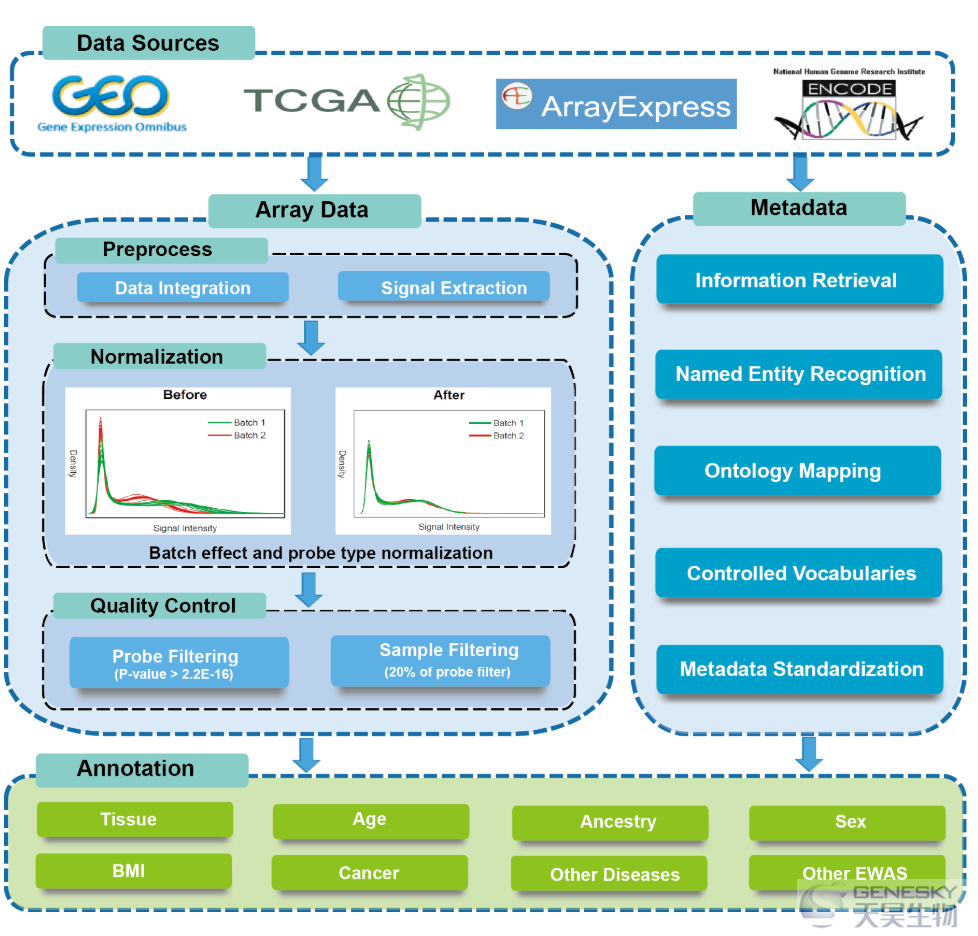
EWAS Data Hub整合了来自
GEO、
TCGA、
ArrayExpress和
ENCODE数据库的共计
75,344个样本的
DNA甲基化芯片数据(450K和850K芯片数据)和相应的元数据,涉及
470种组织/细胞类型,
306种疾病和178种样本相关变量。数据整合处理时采用了
归一化方法来消除不同数据集的批次效应,为
485,512个探针和
36,397个基因提供了参考DNA甲基化图谱。
图:EWAS Data Hub的数据处理流程
● EWAS Data Hub主页 (可以搜索探针,基因或者样本类型)
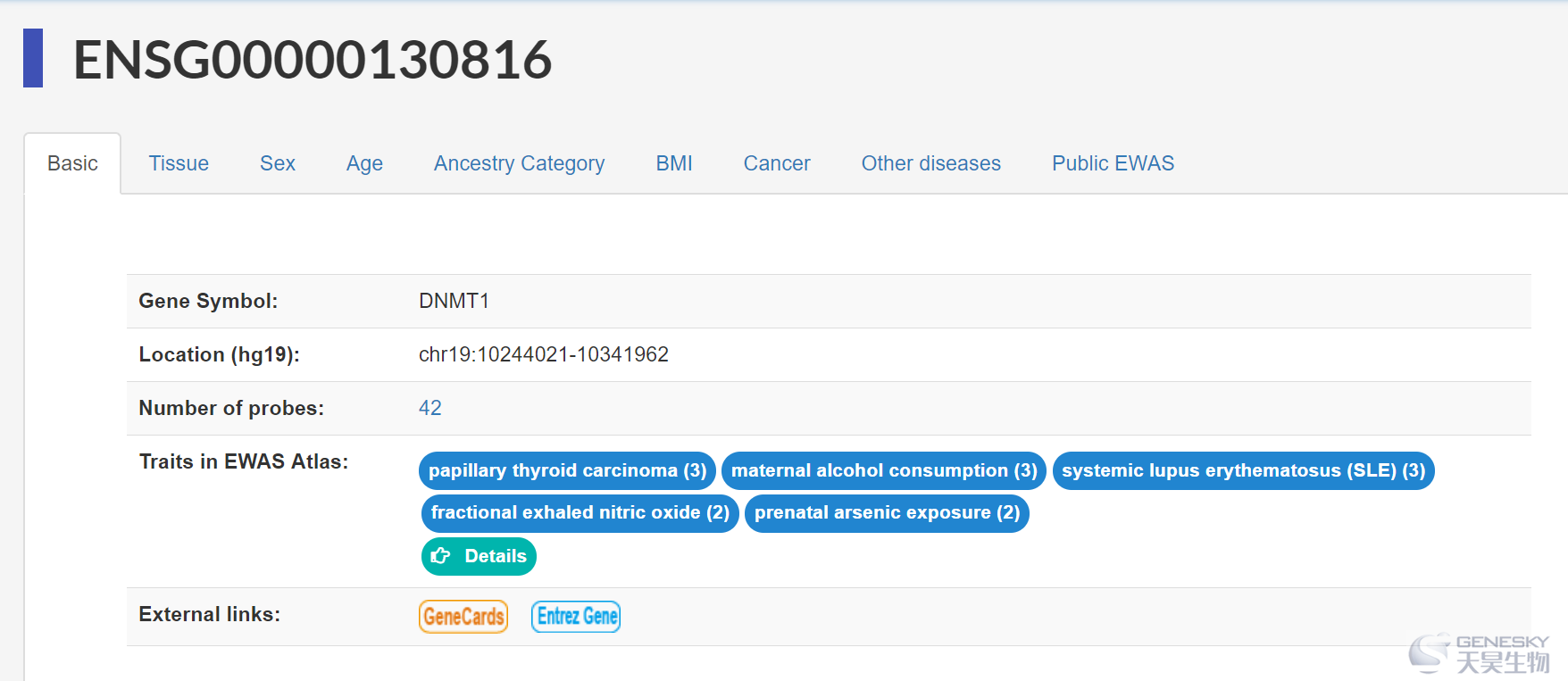
● 搜索示例(DNMT1基因)
图:基因基本信息和基因的探针数
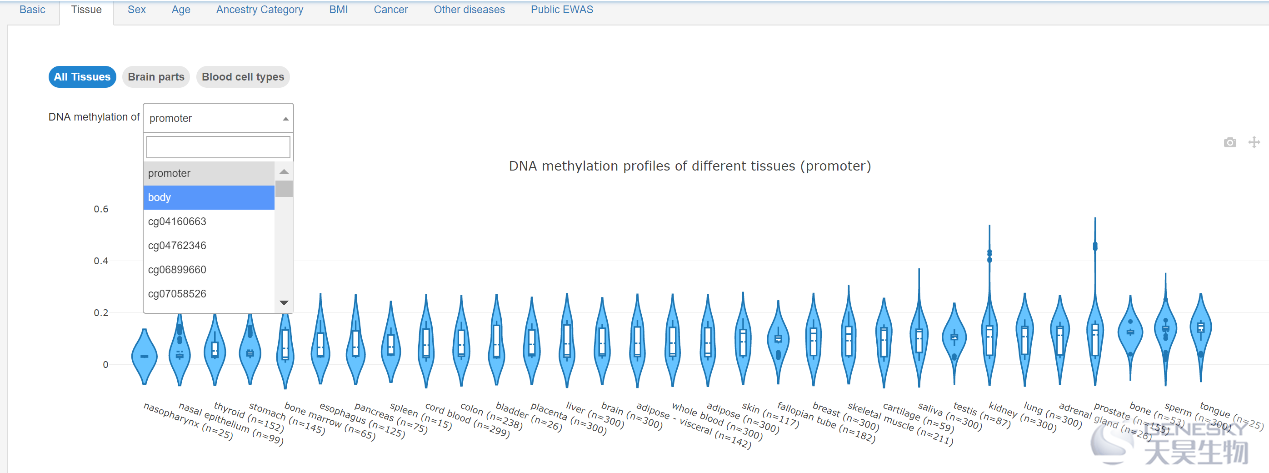
图:不同组织或细胞的甲基化情况(可以选择探针位置和种类)
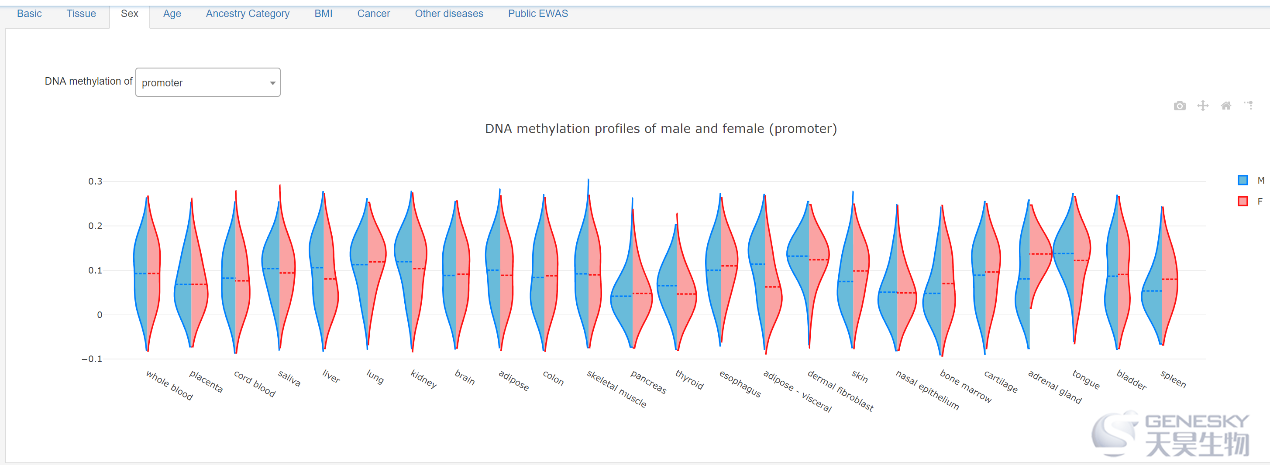
图:不同性别的甲基化差异
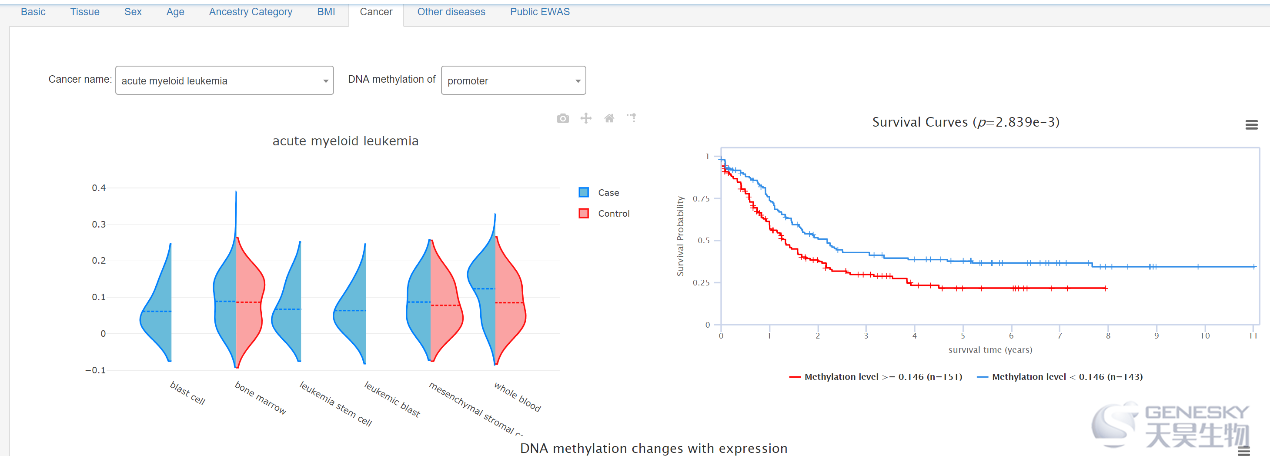
图:基因甲基化和肿瘤相关性,甲基化和生存相关性
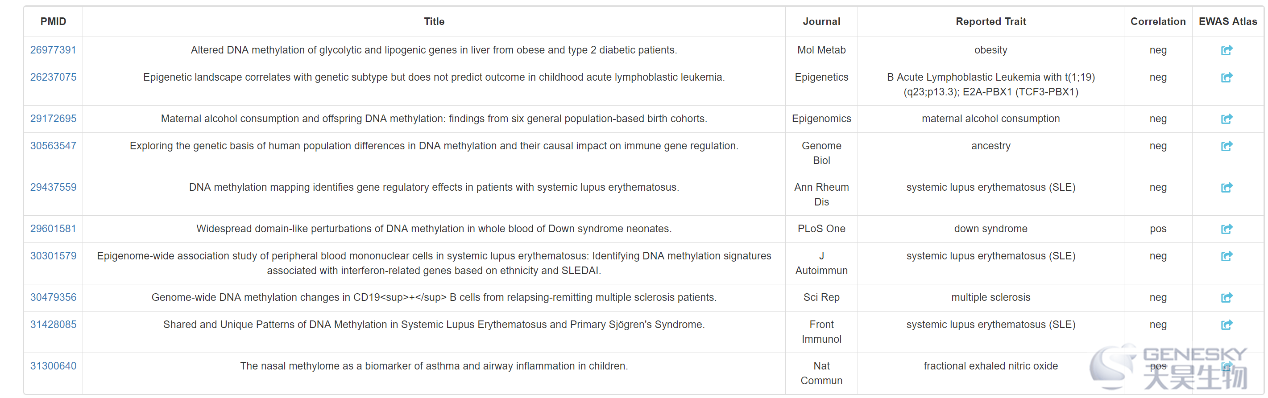
图:基因的甲基化研究文献和结论
结语:好用的数据库进行充分数据挖掘+自己的临床样本进行技术验证(推荐选择多重目的区域甲基化富集测序技术——MethylTarget®,让您的科研成果更上一个台阶!

 咨询热线:400-065-6886
咨询热线:400-065-6886

 咨询热线:400-065-6886
咨询热线:400-065-6886